GWAS基因芯片数据预处理:质量控制(quality control)
内容导读
互联网集市收集整理的这篇技术教程文章主要介绍了GWAS基因芯片数据预处理:质量控制(quality control),小编现在分享给大家,供广大互联网技能从业者学习和参考。文章包含1231字,纯文字阅读大概需要2分钟。
内容图文

一、数据为什么要做质量控制
比起表观学研究,GWAS研究很少有引起偏差的来源,一般来说,一个人的基因型终其一生几乎不会改变的,因此很少存在同时影响表型又影响基因型的变异。但即便这样,我们在做GWAS时也要去除一些可能引起偏差的因素。
这种因素主要有:群体结构、个体间存在血缘关系、技术性操作。
二、怎么看数据是否需要进行质量控制
下面分别为样本和SNP位点在数据中的直方图,当数据不在绝大多数的分布当中时,我们会倾向于认为那是测序、人工操作等其他方面造成的误差,而非该个体的真实情况,因此是需要将这些样本和位点过滤掉的。
这个阈值的设定并没有一个金标准,可参考往年发表的文献的常用阈值。
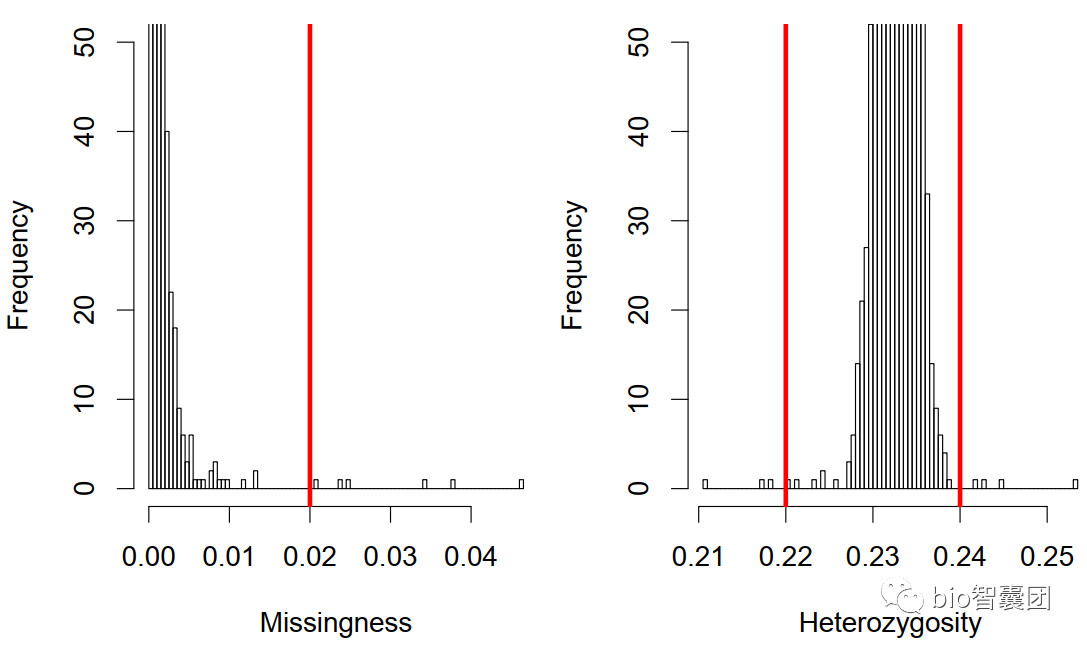
1、样本过滤阈值的设定
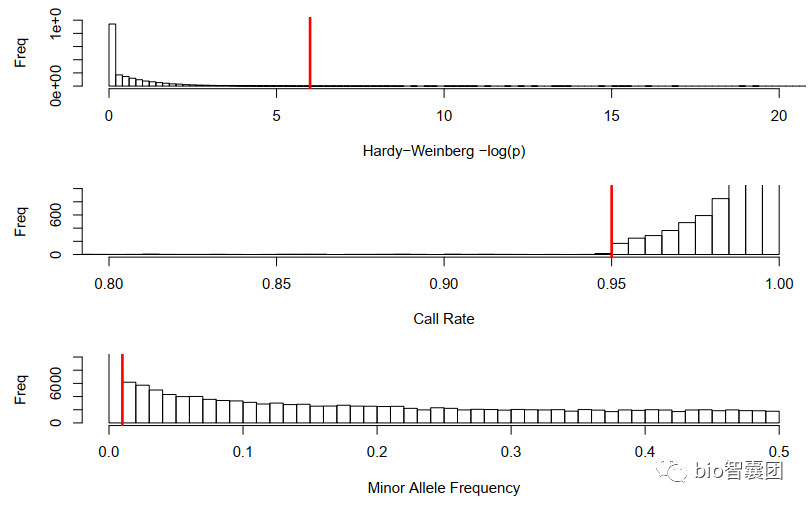
2、SNP过滤阈值的设定
三、怎么进行质量控制
质量控制包括两个方向,一个是样本的质量控制,一个是SNP的质量控制
1、样本的质量控制
样本的质量控制包括:缺失率、杂合性、基因型性别和记录的性别是否一致。
1)检测缺失率,通常情况下,将样本缺失率大于5%的个体去除
plink --bfile file --mind 0.05 --make-bed --out file_mind
2)检测杂合性
plink --bfile file --het --make-bed --out file_het
3) 检测性别不一致的个体
plink --bfile file --check-sex --make-bed --out file_checksex
4)去除不符合的样本
将1-3)获得不符合的样本去除
plink --bfile removesample.txt --remove removesample.txt --make-bed --out file_qcsample
removesample.txt的格式如下:
FID IID
ASN ind1
ASN ind2
2、SNP位点的质量控制
SNP位点的质量控制包括:MAF值、call出率、Hardy-Weinberg Equilibrium
其命令见如下:
plink --bfile file_mind_file_qcsample --hwe 0.00001 --geno 0.02 --maf 0.01 --make-bed --out file_qcsample_snp
--hwe指的是不符合哈温伯格平衡的SNP位点,P值小于0.00001;
--geno指的是基因型缺失率大于2%的样本;
--maf指的是次等位基因频率低于1%的SNP位点;
最后,会得出干净的SNP和样本。
文中图片出处:
https://jvanderw.une.edu.au/Mod2Lecture_PLINK.pdf
原文:https://www.cnblogs.com/chenwenyan/p/10563835.html
内容总结
以上是互联网集市为您收集整理的GWAS基因芯片数据预处理:质量控制(quality control)全部内容,希望文章能够帮你解决GWAS基因芯片数据预处理:质量控制(quality control)所遇到的程序开发问题。 如果觉得互联网集市技术教程内容还不错,欢迎将互联网集市网站推荐给程序员好友。
内容备注
版权声明:本文内容由互联网用户自发贡献,该文观点与技术仅代表作者本人。本站仅提供信息存储空间服务,不拥有所有权,不承担相关法律责任。如发现本站有涉嫌侵权/违法违规的内容, 请发送邮件至 gblab@vip.qq.com 举报,一经查实,本站将立刻删除。
内容手机端
扫描二维码推送至手机访问。